NCBI BLAST
このチュートリアルでは、SnapGene から NCBIデータベースにアクセスし BLAST検索を行う方法、またデータを SnapGene にインポートするを紹介しています。
1.【準備】DNA配列を入手する
任意の配列(500~700 bpぐらいの配列)を各自用意してください。本チュートリアルでは以下の配列を使用します。
SnapGeneにDNA配列をコピーします。SnapGeneの起動から配列のコピーまでは、 プラスミドマップ:プラスミドデータの取得とマップの表示 を参照してください。
2. NCBI BLAST検索
SnapGeneを起動して、メニューにある「編集」から「すべて選択」を選びます。BLAST検索の対象が特定されている場合、「範囲を選択」を選び対象となる配列を指定します。
配列の範囲の選択は、マップビュー または シークエンスビュー から直接行うことも可能です。
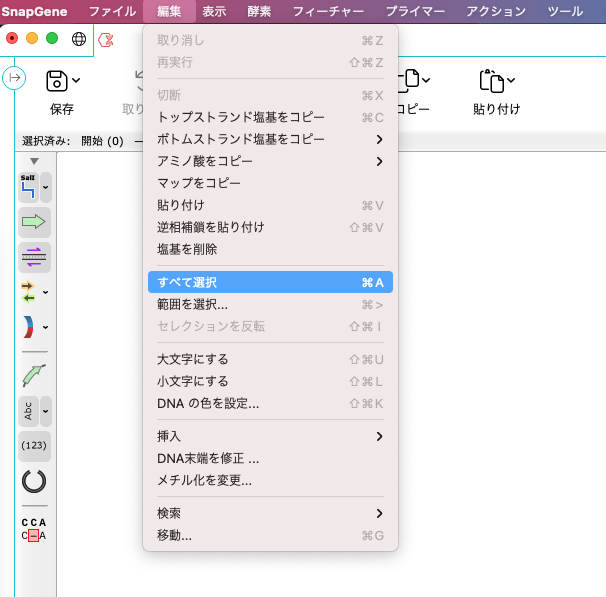
「ツール」→「選択済みのDNAのBLAST」から使用するデータベースを選択すると、ブラウザが起動し NCBI BLAST ページが開きます。
- ヌクレオチドデータベース:選択した塩基配列を塩基配列データベース(blastn)で相同性を持つ配列を検索
- タンパク質データベース:塩基配列をアミノ酸配列に翻訳し、アミノ酸配列データベース(blastx)で相同性を持つ配列を検索
- 翻訳済みのヌクレオチドデータベース:塩基配列からアミノ酸に翻訳し、塩基配列もアミノ酸に翻訳されたデータベース(tblastx)で、アミノ酸同士を比較し相同性を持つ配列を検索
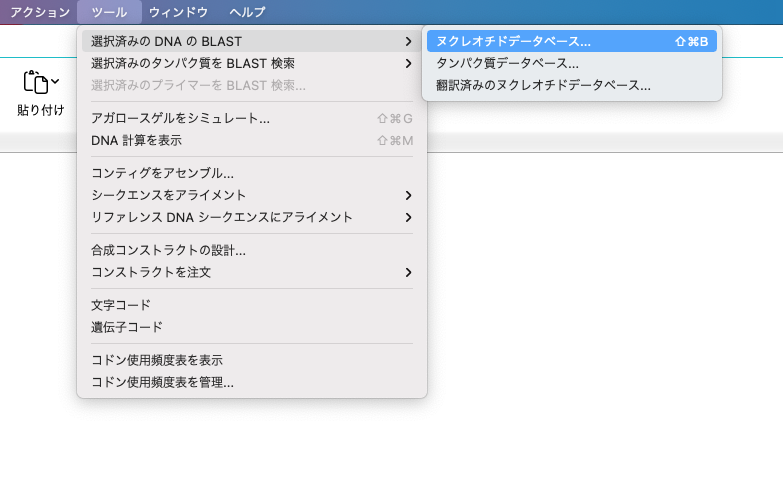
NCBIデータベースのタブが開き、選択された配列(または翻訳)が、 Query Sequenceとして検索フィールドに自動で貼り付けられます。
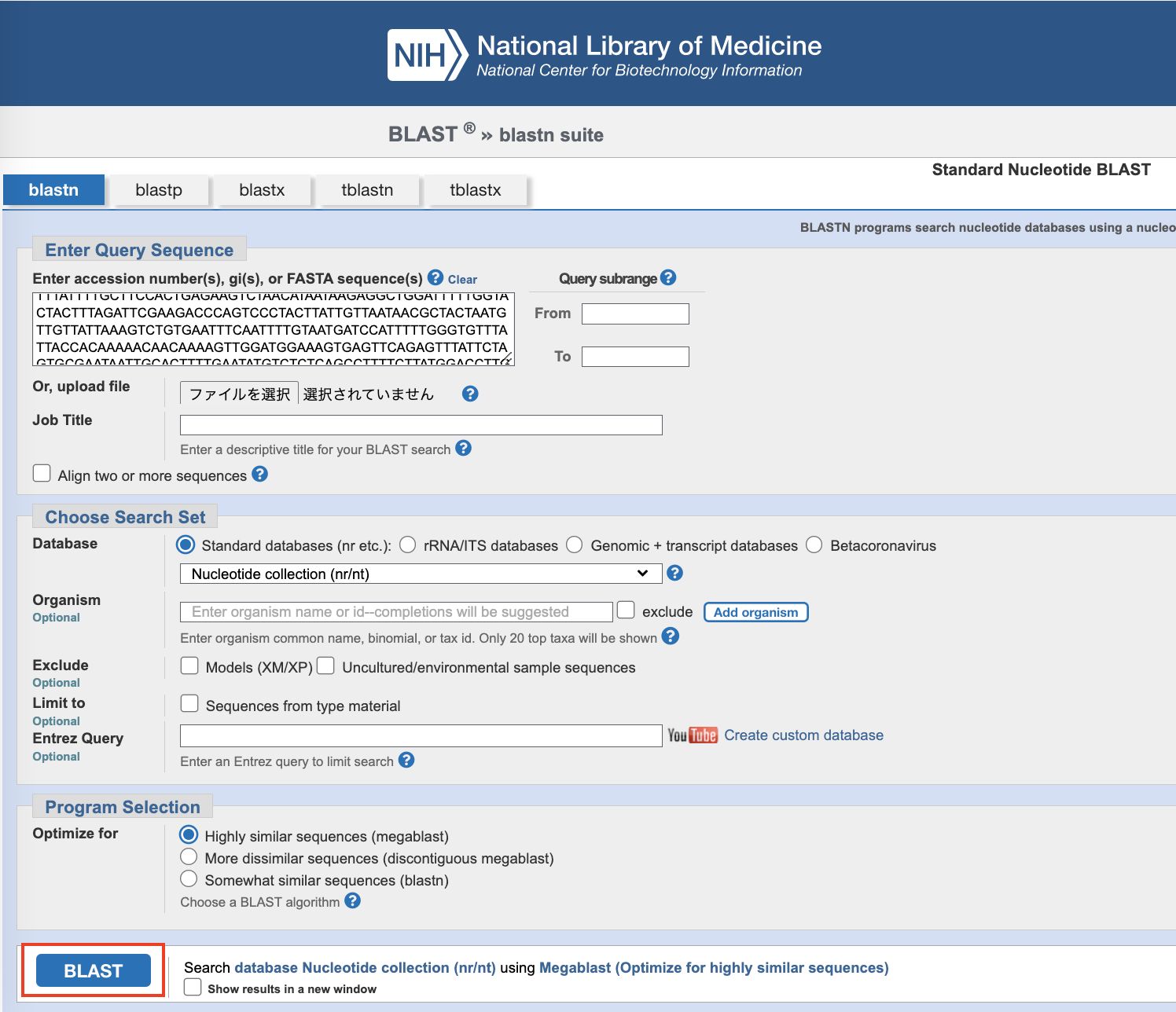
必要に応じてパラメータを設定後、BLAST ボタンをクリックして BLAST検索を実行します。
3. NCBIからのインポート
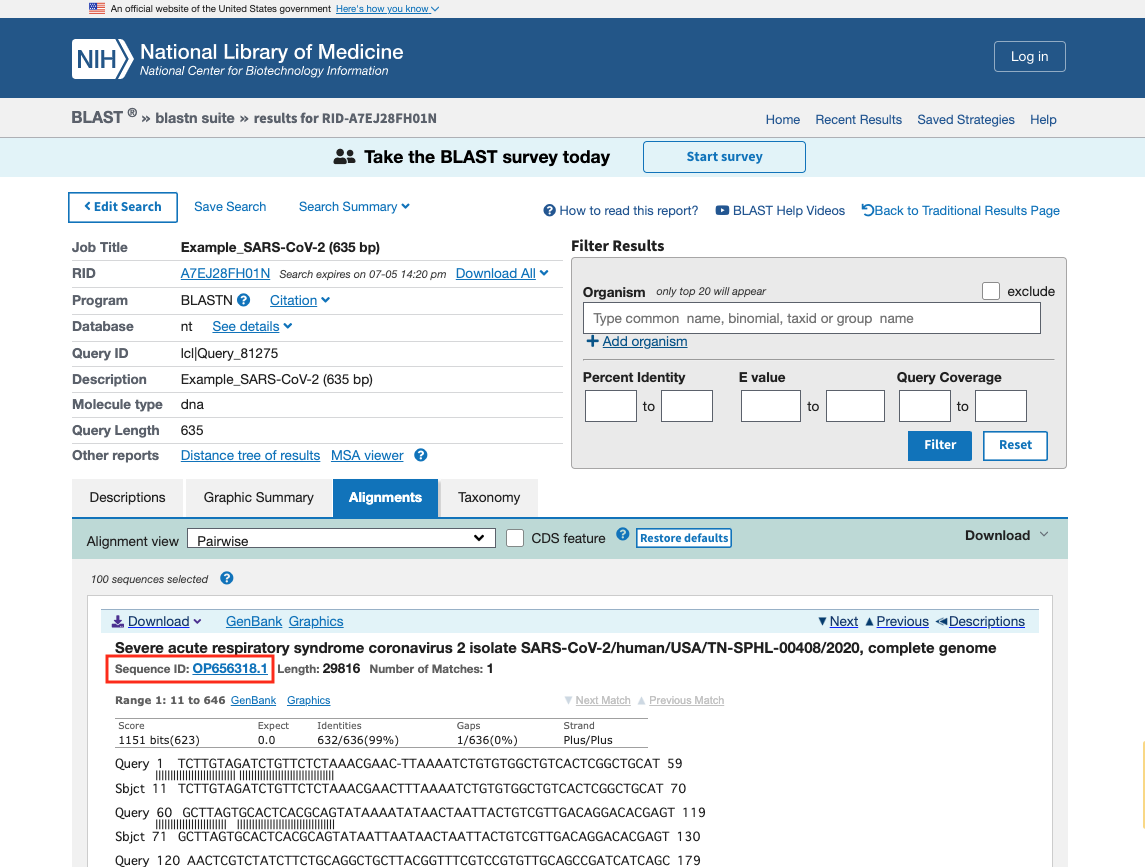
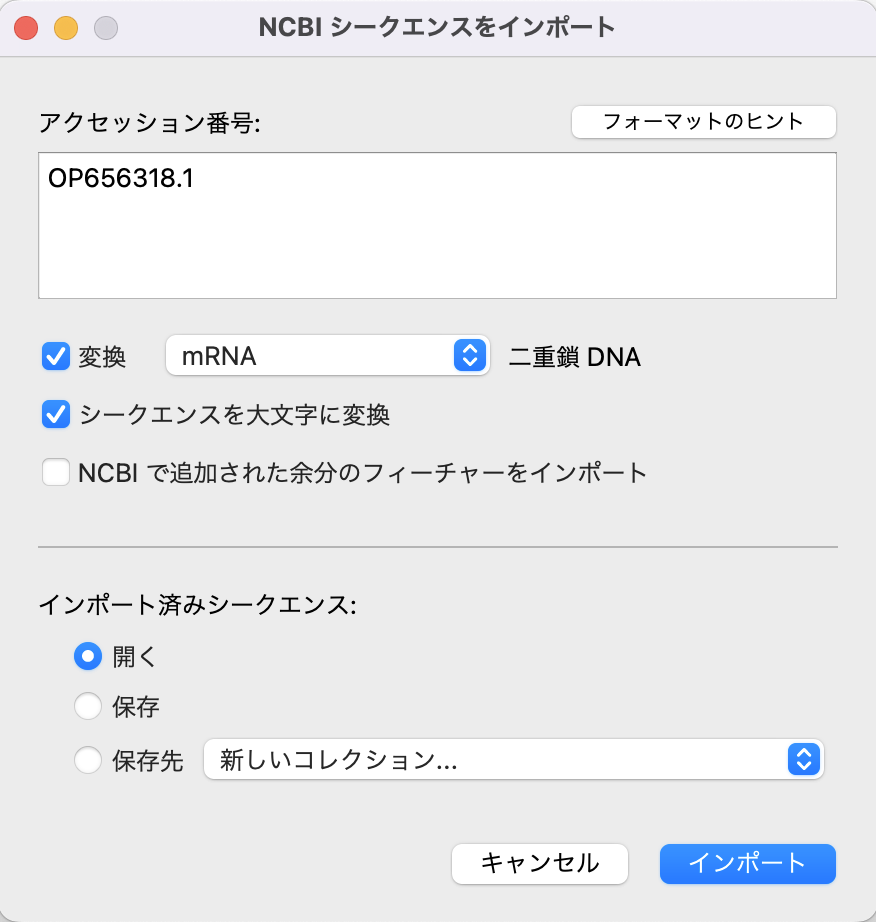
検索結果としてヒットしたNCBIの配列情報を SnapGene にインポートするには、アクセッション番号を使用します。
SnapGene のツールバーの「ファイル」→ 「インポート」から 「NCBIシークエンス」を選択します。
「アクセッション番号:」のフィールドに、アクセッション番号を入力し、インポートボタンをクリックします。
NCBIの配列情報が SnapGene にインポートされます。


